# Librerias
library(readxl) # Para leer los excels
library(dplyr) # Para tratamiento de dataframes
library(caret) # train/test data
library(psych) # test mardia /kmo
library(ggcorrplot)
library(GPArotation) # Para poder rotar los factores
library(lavaan) # cfa
library(semPlot) # diagrama cfaReducción Dimensionalidad - Análisis Factorial: ECV_factorial
Introducción
A continuación se expondrá como llevar a cabo una Reducción de Dimensionalidad utilizando un Análisis Factorial. Para ello se utilizará un dataset sobre el que se irán explicando los sucesivos pasos a llevar a cabo.
dataset
En este cuaderno vamos a analizar el dataset llamado ECV_factorial.xlsx. Este dataset presenta un conjunto de microdatos relativos a la Encuesta de Condiciones de Vida (ECV) donde se puntúa el nivel de satisfacción en determinados ámbitos de la vida (laboral, económico, relaciones personales..). El objetivo es llevar a cabo un análisis factorial.
Concretamente en este dataset tenemos las siguientes variables:
- PB030: Identificación transversal de la persona.
- PW010: Grado de satisfacción con su vida en la actualidad.
- PW030: Grado de satisfacción con la situación económica en su hogar.
- PW040: Grado de satisfacción con su vivienda.
- PW100: Grado de satisfacción con su trabajo actual.
- PW120: Grado de satisfacción con el tiempo que dispone para hacer lo que le gusta.
- PW160: Grado de satisfacción con sus relaciones personales.
- PW200: Grado de satisfacción con las áreas recreativas o verdes de la zona en la que vive.
- PW210: Grado de satisfacción con la calidad de la zona en la que vive.
Excepto la primera variable, todas ellas están codificadas desde 0 (Nada satisfecho) hasta 10 (Plenamente satisfecho) y 99 NO sabe.
Descripción del trabajo a realizar
Se pretende hacer un Análisis de Reducción de la Dimensionalidad empleando el procedimiento de Análisis Factorial.
Hacer un análisis exploratorio.
Dividir datos en dos partes
Análisis Factorial Exploratorio (EFA)
- Estimación matriz correlaciones.
- Verificar que la matriz sea factorizable.
- Método de extracción de factores.
- Número de factores a extraer.
- Extracción factores + rotación.
Análisis Factorial Confirmatorio (CFA)
- Método de extracción de factores.
- Probar una o varias estructuras factoriales.
Análisis Exploratorio (EDA)
EDA viene del Inglés Exploratory Data Analysis y son los pasos relativos en los que se exploran las variables para tener una idea de que forma toma el dataset.
Cargar Librerías
Lo primero de todo vamos a cargar las librerías necesarias para ejecutar el resto del código del trabajo:
Lectura datos
Ahora cargamos los datos del excel correspondientes a la pestaña “Datos” y vemos si hay algún NA o algún valor igual a 0 en nuestro dataset. Vemos que no han ningún NA (missing value) en el dataset luego no será necesario realizar ninguna técnica para imputar los missing values o borrar observaciones.
datos <- read_excel("../../../../files/ECV_factorial.xlsx", sheet = "Datos")En primer lugar, cargamos los datos que vamos a utilizar. En este caso, se trata de un conjunto de datos compuesto por 26883 filas y 9 columnas. Las filas corresponden a individuos concretos y las 14 columnas a variables mencionadas previamente.
Antes de comenzar a aplicar la técnica, comprobamos si hay valores perdidos, por si fuera necesario realizar algún preproceso. En este caso, y como vemos a continuación vemos que si hay valores NA, y por ello los imputaremos con el algoritmo que usemos después.
sum(is.na(datos))[1] 26341Por otra parte, para tener una noción general que nos permita describir el conjunto con el que vamos a trabajar, podemos extraer su dimensión, el tipo de variables que contiene o qué valores toma cada una.
# Dimensión del conjunto de datos
dim(datos)[1] 26883 9# Tipo de variables que contiene
str(datos)tibble [26,883 × 9] (S3: tbl_df/tbl/data.frame)
$ PB030: num [1:26883] 101 102 103 201 202 301 302 401 402 501 ...
$ PW010: num [1:26883] 8 8 7 10 10 5 5 8 8 6 ...
$ PW030: num [1:26883] 8 8 7 4 4 5 8 0 0 6 ...
$ PW040: num [1:26883] 8 8 7 8 7 6 8 8 8 8 ...
$ PW100: num [1:26883] 8 NA 7 10 9 NA NA NA NA NA ...
$ PW120: num [1:26883] 8 8 5 10 6 8 NA 8 5 10 ...
$ PW160: num [1:26883] 8 8 7 10 10 8 8 8 8 8 ...
$ PW200: num [1:26883] 8 8 7 5 8 8 8 8 10 8 ...
$ PW210: num [1:26883] 8 8 7 5 8 7 7 8 8 8 ...# Descripción de las variables
summary(datos) PB030 PW010 PW030 PW040
Min. : 101 Min. : 0.000 Min. : 0.000 Min. : 0.000
1st Qu.: 369651 1st Qu.: 6.000 1st Qu.: 5.000 1st Qu.: 6.000
Median : 748903 Median : 7.000 Median : 6.000 Median : 8.000
Mean : 783591 Mean : 6.898 Mean : 5.801 Mean : 7.349
3rd Qu.:1180002 3rd Qu.: 8.000 3rd Qu.: 7.000 3rd Qu.: 8.000
Max. :1711204 Max. :10.000 Max. :10.000 Max. :10.000
NA's :1377 NA's :1386 NA's :1396
PW100 PW120 PW160 PW200
Min. : 0.000 Min. : 0.000 Min. : 0.000 Min. : 0.00
1st Qu.: 6.000 1st Qu.: 5.000 1st Qu.: 7.000 1st Qu.: 5.00
Median : 7.000 Median : 7.000 Median : 8.000 Median : 7.00
Mean : 6.962 Mean : 6.653 Mean : 7.821 Mean : 6.65
3rd Qu.: 8.000 3rd Qu.: 8.000 3rd Qu.: 9.000 3rd Qu.: 8.00
Max. :10.000 Max. :10.000 Max. :10.000 Max. :10.00
NA's :16589 NA's :1408 NA's :1394 NA's :1402
PW210
Min. : 0.000
1st Qu.: 6.000
Median : 8.000
Mean : 7.251
3rd Qu.: 8.000
Max. :10.000
NA's :1389 Como vamos a hacer un doble Análisis Factorial - Exploratorio y Confirmatorio - vamos a dividir la muestra en aproximadamente el 50%, realizando el Exploratorio sobre una mitad, y el Confirmatorio sobre la otra, para ver si los resultados concuerdan.
# Seed para garantizar la reproducibilidad
set.seed(2021)
# Partición de datos aleatoria (identificadas mediante la columna de ID del alumno)
subconjunto.ids <- createDataPartition(datos$PB030, p = 0.5, list = F)
# Para el Exploratorio solo conservamos las observaciones cuyos IDs han sido muestreados
datos_AFE <- datos[subconjunto.ids, ]
dim(datos_AFE) # 13443 observaciones[1] 13443 9# Para el Confirmatorio solo conservamos las observaciones cuyos IDs no han sido muestreados
datos_AFC <- datos[-subconjunto.ids, ]
dim(datos_AFC) # 13440 observaciones[1] 13440 9# Eliminamos la columna de IDs, ya que no nos hace falta:
datos_AFE$PB030 <- NULL
datos_AFC$PB030 <- NULLAnálisis Factorial Exploratorio (EFA)
Introducción
El objetivo de la Reducción de la dimensionalidad es reducir la complejidad de conjuntos de datos con múltiples variables. Su objetivo es transformar variables correlacionadas en un conjunto menor de dimensiones sin perder la mayor parte de la información original.
El Análisis Factorial Exploratorio (Exploratory Factorial Analysis) es un método para reducir la dimensionalidad de un conjunto de variables/indicadores, es decir, es un método para resumir la información. En este sentido, puede confundirse con el Análisis de Componentes Principales (PCA).
El PCA parte de la varianza total para encontrar combinaciones lineales entre las variables originales que expliquen la mayor parte de dicha varianza total. Así, el primer componente principal sería aquella combinación lineal de variables que explica un mayor porcentaje de varianza total; el segundo componente principal sería aquel que explica la mayor proporción de varianza no explicada por el primero, y así sucesivamente. Al aplicar PCA a un conjunto de datos conseguimos pues resumir la información en unas pocas componentes principales. Dichas componentes principales, al ser combinaciones lineales de variables, resultan, muchas veces, difíciles de interpretar.
Por su parte, el EFA distingue entre varianza común y varianza específica. La varianza común o compartida es aquella parte de la variabilidad total de los datos que está compartida entre las variables; mientras, la varianza no compartida es la específica de cada variable. Los factores comunes son, por tanto, variables subyacentes - no observadas - que explican la asociación entre las variables.
Asimismo, desde el punto de vista de las variables, decimos que la comunalidad de una variable es la parte de su varianza explicada por los factores comunes. Por ello, interesa que este dato sea alto. Por el contrario, la especificidad es la parte de variabilidad de una variable específica de dicha variable. Esta última conviene pues que sea baja.
Los factores sí suelen tener una interpretación más sencilla que los componentes principales. Asimismo, mientras los componentes principales, por definición, no están correlacionados, los factores pueden estarlo.
El EFA suele utilizarse con datos procendentes de encuestas sociales, psicológicas o sanitarias, sin embargo, también puede aplicarse a otros tipos de datos. En nuestro caso tenemos datos procedentes de una encuesta de carácter sociodemográfico.
Los pasos generales son:
Paso 1: Estimación de la matriz de correlaciones.
Dependiendo del tipo de datos que tengamos, debemos utilizar un tipo de correlación u otro:
Datos continuos: La matriz de correlaciones de Pearson y la de Spearman son las más apropiadas ante continuos o ante datos ordinales (categóricos) con más de 7 categorías de respuesta (tienden a la continuidad).
Datos categóricos/ordinales: la matriz de correlaciones policórica es la más recomendada ante datos ordinales de 7 o menos categorías de respuesta. Si tuviéramos datos dicotómicos, la matriz a emplear sería la matriz tetracórica (similar a la policórica pero con datos dicotómicos).
En nuestro caso, como tenemos datos ordinales con 11 opciones de respuesta (del 0 al 10), usaremos la matriz de correlaciones de Pearson.
matriz_correlaciones <- cor(datos_AFE, method = "pearson", use = "complete.obs")
ggcorrplot(matriz_correlaciones, lab = T)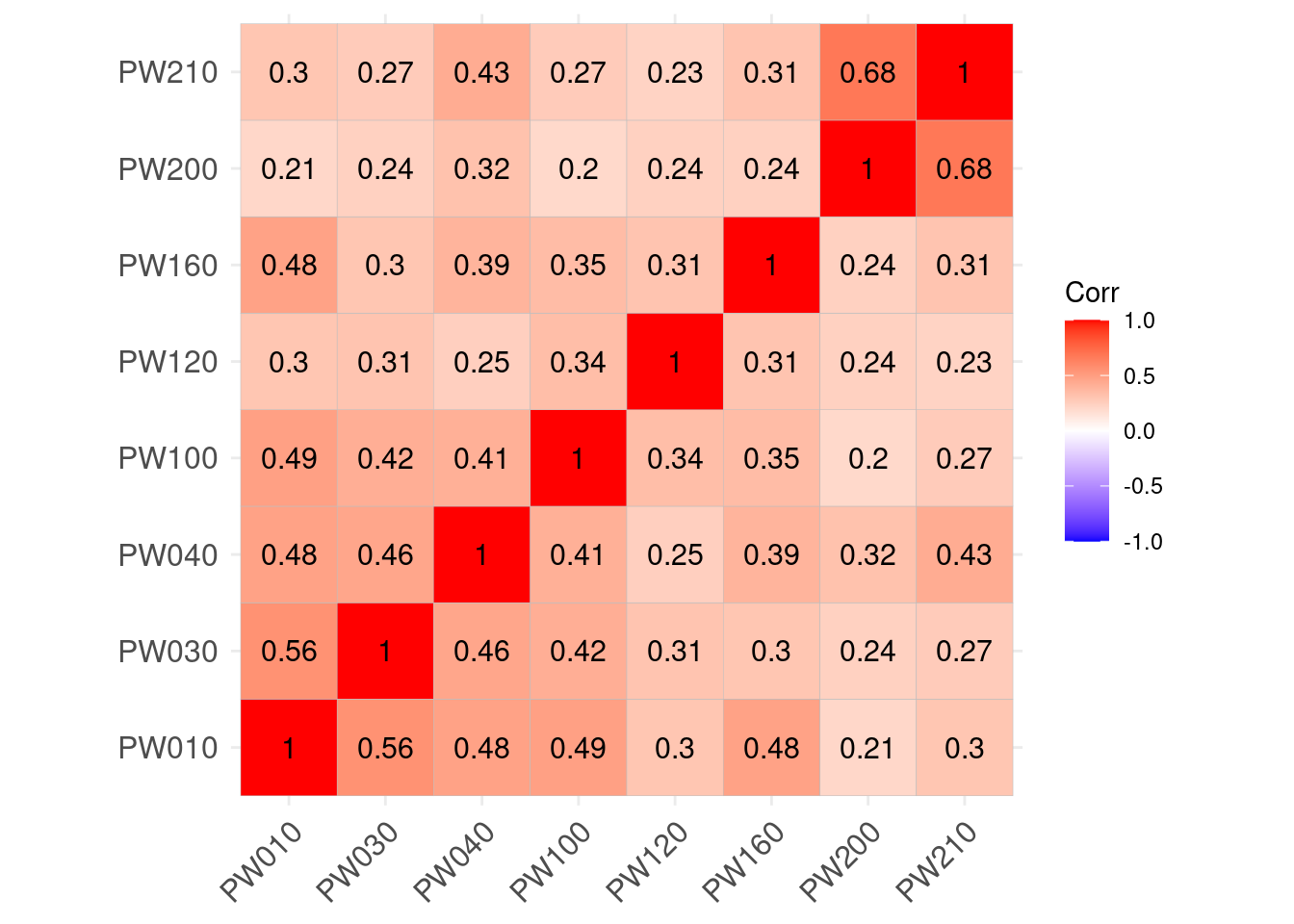
Todas las correlaciones son positivas y, en general, no son muy altas.
Paso 2: Verificar que la matriz sea factorizable (es decir, que tiene sentido hacer un AFE con nuestros datos):
Si la matriz no fuese factorizable, la relación entre las variables sería tan baja que no se formarían factores.
Entre los métodos para comprobar si la matriz es factorizable destacan:
Test de esfericidad de Bartlett: se pregunta si la matriz de correlaciones es o no la matriz identidad. Si la matriz de correlaciones es la matriz identidad, las variables no estarían correlacionadas y no habría varianza compartida de la que extraer los factores (no habría factores comunes). Si rechazamos la hipótesis nula (la matriz de correlaciones es la matriz identidad), la matriz será factorizable.
Medida KMO (Kaiser-Meyer-Olkin): expresa el grado de predicción de las variables a partir de las demás. Su valor oscila entre 0 y 1. Cuanto mayor sea, mejor. Valores a partir de 0,5 se consideran aceptables.
Calcular el determinante de la matriz de correlaciones: valores cercanos a cero indican que la matriz es factorizable.
# Test de esfericidad de Bartlett:
p_esf <- cortest.bartlett(matriz_correlaciones, n = nrow(datos_AFE))
cat("El p-valor del test de esfiricidad de Bartlett es: ", p_esf$p.value, "\n")El p-valor del test de esfiricidad de Bartlett es: 0 # KMO:
KMO(matriz_correlaciones)Kaiser-Meyer-Olkin factor adequacy
Call: KMO(r = matriz_correlaciones)
Overall MSA = 0.8
MSA for each item =
PW010 PW030 PW040 PW100 PW120 PW160 PW200 PW210
0.81 0.83 0.88 0.89 0.88 0.86 0.67 0.70 # Determinante de la matriz:
cat("El valor del determinante de la matriz es: ", det(matriz_correlaciones))El valor del determinante de la matriz es: 0.08410902El p-valor es menor a los niveles de significación habituales(10%, 5% y 1%) por lo que rechazamos la hipótesis nula: la matriz de correlaciones no es la matriz identidad.
- El resultado del KMO es bueno: 0,80.
- El determinante tiene un valor bastante bajo.
- Los test muestran que la matriz es factorizable.
Paso 3: Determinar un método de extracción de factores:
La ecuación del modelo factorial es la siguiente:
\[X_j = a_{j1}F_1 + a_{j2}F_2+ ... +a_{j n}F_n + u_j\]
Donde \(X_j\) (variable j) es una combinación lineal de factores comunes y del factor único (especificidad). Los \(a_{jh}\) son los pesos factoriales, que representan la importancia que cada factor común tiene en explicar la variable \(X_j\).
El objetivo de los métodos de extracción de factores es reproducir, con el mínimo error, la matriz de correlaciones a partir de la matriz de pesos factoriales.
Existen varios métodos de extracción de factores. Los más comunes son:
Máxima Verosimilitud (Maximum Likelihood, ML). Para utilizarlo, nuestros datos deben seguir una normal multivariante (lo que podemos comprobar realizando el test de Mardia, por ejemplo). Estadísticamente es el más adecuado, pues es asintóticamente insesgado, eficiente y consistente.
Mínimos Cuadrados No Ponderados (Unweighted Least Squares, ULS) (También llamado Residuos Mínimos, MinRes). No requiere de la existencia de normalidad multivariante.
Ejes principales. Tampoco requiere de datos que sigan una normal multivariante.
Componentes principales. Como hemos dicho en la introducción, no es método de ánalisis factorial propiamente dicho, ya que su objetivo es intentar explicar toda la varianza, y no solo la varianza común o compartida. Sin embargo, su uso, aunque no se recomiende, está bastante extendido, pues es la opción por defecto de muchos programas estadísticos.
# Test de Mardia:
mardia(datos_AFE, na.rm = TRUE)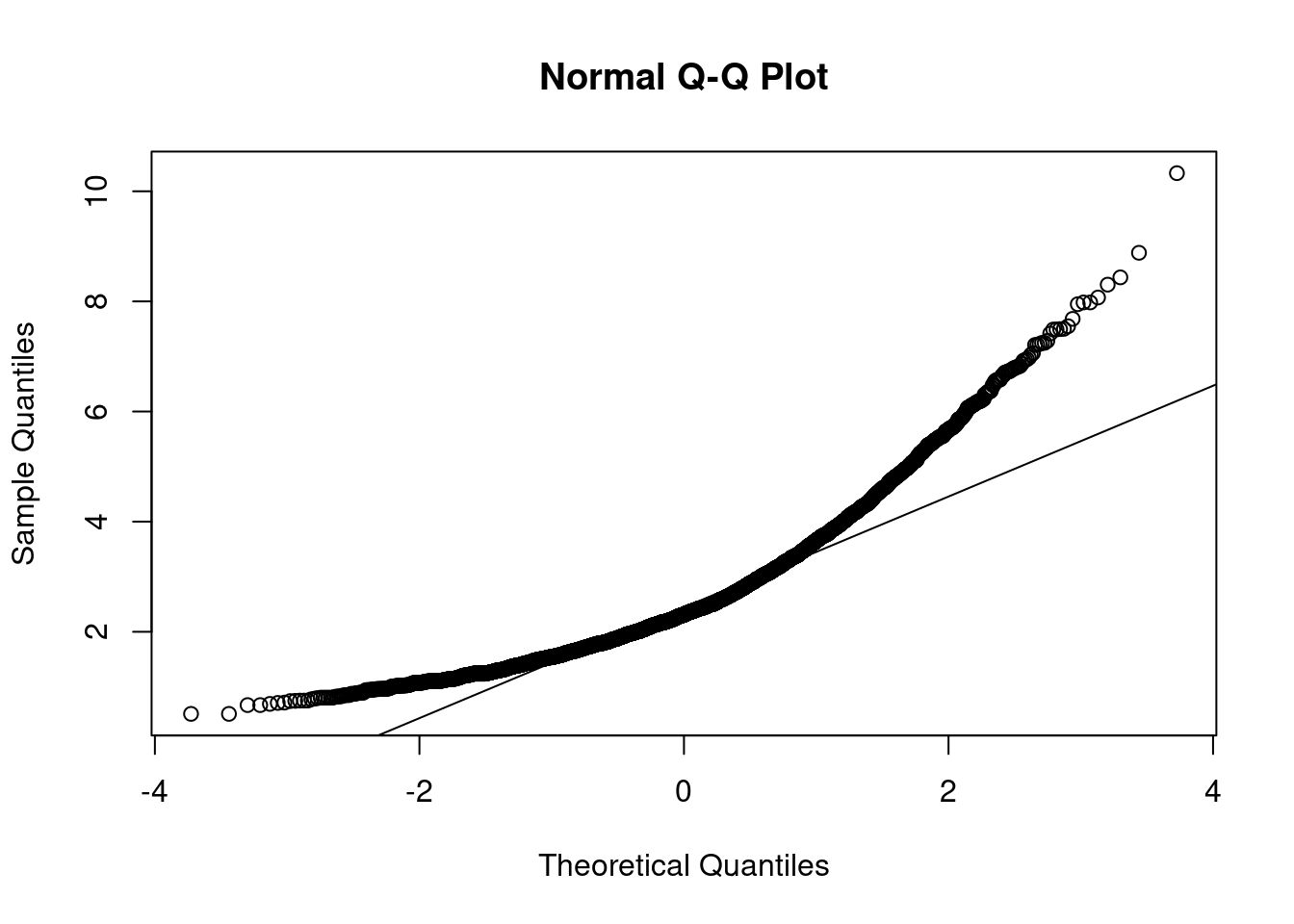
Call: mardia(x = datos_AFE, na.rm = TRUE)
Mardia tests of multivariate skew and kurtosis
Use describe(x) the to get univariate tests
n.obs = 5157 num.vars = 8
b1p = 11.34 skew = 9750.3 with probability <= 0
small sample skew = 9757.24 with probability <= 0
b2p = 130.3 kurtosis = 142.78 with probability <= 0ks.test(datos_AFE, pnorm)
Asymptotic one-sample Kolmogorov-Smirnov test
data: datos_AFE
D = 0.95804, p-value < 2.2e-16
alternative hypothesis: two-sidedComo los p-valores son inferiores a los niveles de significación habituales (10%, 5% y 1%) se rechaza la hipótesis nula, es decir, se rechaza la normalidad de los datos. También podemos comprobar este hecho haciendo uso del Q-Q plot, ya que la línea de puntos está bastante alejada de la recta que refleja la normal. O lo que e lo mismo, hay mas de un 5% de datos fuera de la diagonal, leugo con un 95% de confianza podremos decir que no se asemeja con una normal.
Como no existe normalidad, debemos emplear un método de extracción de factores robusto la inexistencia de la misma, como es ULS (Mínimos Cuadrados No Ponderados).
Paso 4: Determinamos el número de factores a extraer:
Existen cuatro métodos principales:
- Regla de Kaiser: se deben aceptar todos aquellos factores con un autovalor mayor a 1.
- Gráfico de sedimentación (scree plot): gráfico donde podemos ver cómo disminuye la varianza explicada o el autovalor a medida que vamos aumentando el número de factores a extraer. Se complementa muy bien con la regla de Kaiser.
- Establecimiento de un porcentaje de varianza explicada mínimo (por ejemplo, el 75%): cogeríamos todos los factores necesarios para explicar ese porcentaje mínimo de varianza.
- Análisis paralelo (AP, método recomendado): el AP parte de generar nuevas muestras aleatorias (mínimo 100) con el mismo número de variables y observaciones que la muestra original y, a partir de ello, se queda con aquellos factores cuyo autovalor es superior a los generados por azar.
Emplearemos el Análisis Paralelo al ser el método más recomendado.
fa.parallel(matriz_correlaciones, n.obs = nrow(datos_AFE), n.iter = 500, fa = "fa", fm = "uls")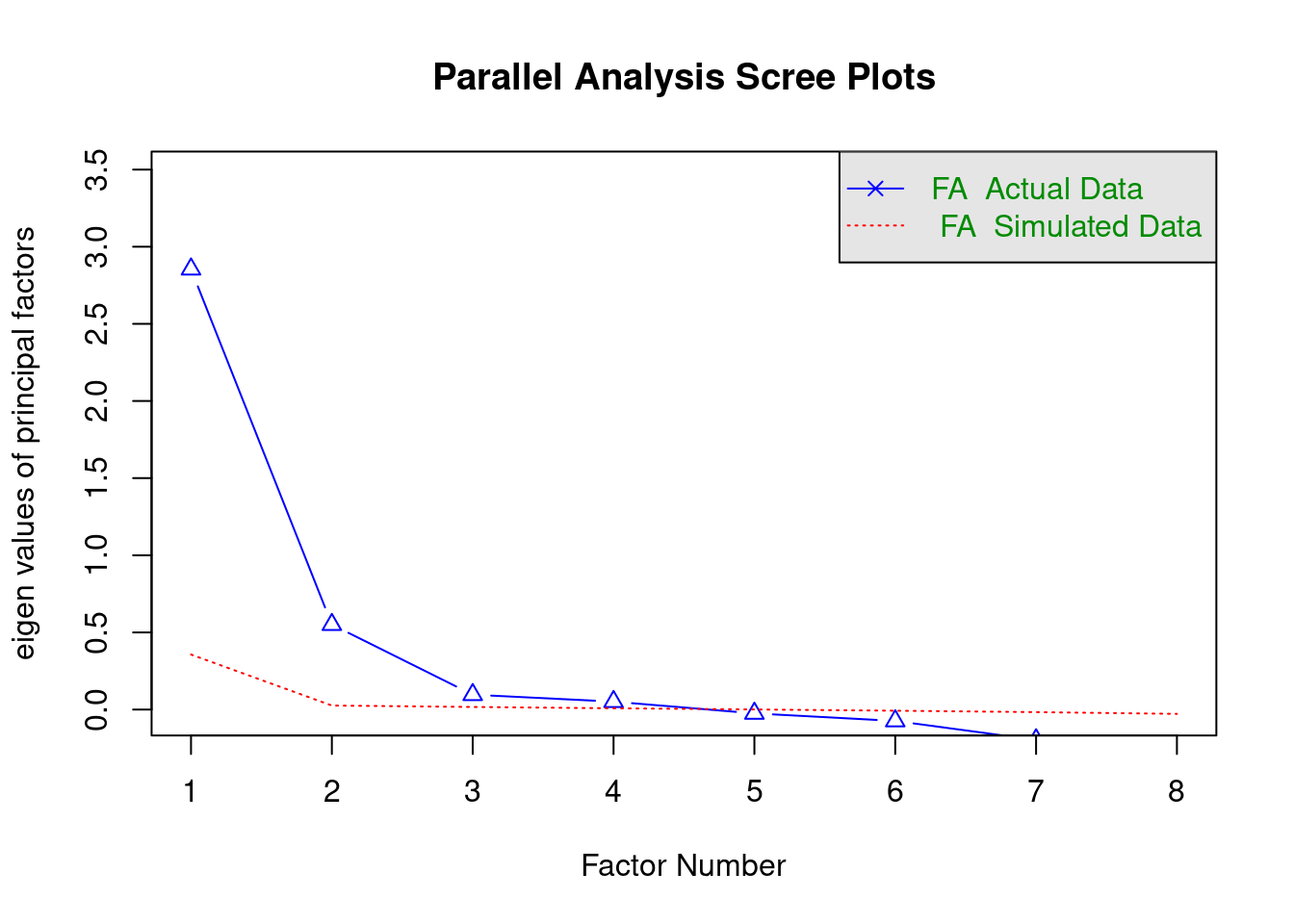
Parallel analysis suggests that the number of factors = 4 and the number of components = NA # uls lleva a cabo un método de minimal residuals
# fa = "fa" show the eigen values for a principal axis factor analysisEl Análisis Paralelo sugiere la extracción de 4 factores.
Paso 5: Extracción de factores + rotación:
Vamos a extraer tres factores, siguiendo lo recomendado por el Análisis Paralelo.
Asimismo, debemos decidir si vamos a rotar los factores y qué tipo de rotación vamos a emplear. Los métodos de rotación facilitan la interpretación de los factores, ya que sin rotarlos, suele ser muy difíciles de interpretar, por lo que se recomienda el uso de dichas técnicas de rotación.
Existen dos tipos de rotación:
- Rotación oblicua: permite que los factores puedan tener correlación entre ellos. Tipo recomendado, ya que es el más cercano a la estructura real que deseamos explorar. Un ejemplo es el método oblimin.
- Rotación ortogonal: fuerza a los factores a que no puedan tener correlación entre ellos. Un ejemplo es el método varimax.
Probaremos los dos y nos quedaremos con la solución que mejor resultado arroje. Pero, ¿cómo determinamos qué solución factorial ajusta mejor?
- Fijándonos en los pesos factoriales: Cuanto mayor sea el peso factorial de un ítem en un factor mejor. Se aceptan pesos factoriales por encima de 0,4. En general, una buena solución presentará variables que pesan mucho en un factor y poco en el resto.
- Índices de bondad del ajuste. Existen unos cuantos, pero nos podemos fijar en RMSEA, SRMR, TLI y CFI. RMSEA y SRMR cuantos más bajos mejor (se aceptan valores por debajo de 0,08), y TLI y CFI cuantos más altos mejor (valores por encima de 0,95 se consideran muy buenos).
# Rotación oblicua oblimin:
AFE_oblimin <- fa(matriz_correlaciones, nfactors = 4, n.obs = nrow(datos_AFE), rotate = "oblimin", fm = "uls", alpha = 0.05)
AFE_obliminFactor Analysis using method = uls
Call: fa(r = matriz_correlaciones, nfactors = 4, n.obs = nrow(datos_AFE),
rotate = "oblimin", fm = "uls", alpha = 0.05)
Standardized loadings (pattern matrix) based upon correlation matrix
ULS1 ULS2 ULS4 ULS3 h2 u2 com
PW010 0.77 -0.06 0.09 -0.02 0.65 0.3543 1.0
PW030 0.01 0.01 0.98 0.01 1.00 0.0045 1.0
PW040 0.49 0.22 0.09 -0.03 0.44 0.5587 1.5
PW100 0.52 0.01 0.06 0.10 0.38 0.6242 1.1
PW120 0.01 0.00 0.01 0.99 1.00 0.0045 1.0
PW160 0.64 0.07 -0.14 0.07 0.39 0.6099 1.2
PW200 -0.07 0.74 0.05 0.06 0.55 0.4544 1.0
PW210 0.04 0.92 -0.02 -0.03 0.87 0.1317 1.0
ULS1 ULS2 ULS4 ULS3
SS loadings 1.63 1.51 1.07 1.05
Proportion Var 0.20 0.19 0.13 0.13
Cumulative Var 0.20 0.39 0.53 0.66
Proportion Explained 0.31 0.29 0.20 0.20
Cumulative Proportion 0.31 0.60 0.80 1.00
With factor correlations of
ULS1 ULS2 ULS4 ULS3
ULS1 1.00 0.44 0.62 0.40
ULS2 0.44 1.00 0.28 0.26
ULS4 0.62 0.28 1.00 0.29
ULS3 0.40 0.26 0.29 1.00
Mean item complexity = 1.1
Test of the hypothesis that 4 factors are sufficient.
df null model = 28 with the objective function = 2.48 with Chi Square = 33268.91
df of the model are 2 and the objective function was 0.01
The root mean square of the residuals (RMSR) is 0.01
The df corrected root mean square of the residuals is 0.03
The harmonic n.obs is 13443 with the empirical chi square 53.96 with prob < 1.9e-12
The total n.obs was 13443 with Likelihood Chi Square = 111.81 with prob < 5.3e-25
Tucker Lewis Index of factoring reliability = 0.954
RMSEA index = 0.064 and the 95 % confidence intervals are 0.052 0.076
BIC = 92.8
Fit based upon off diagonal values = 1
Measures of factor score adequacy
ULS1 ULS2 ULS4 ULS3
Correlation of (regression) scores with factors 0.90 0.94 1.00 1.00
Multiple R square of scores with factors 0.81 0.89 1.00 1.00
Minimum correlation of possible factor scores 0.62 0.78 0.99 0.99fa.diagram(AFE_oblimin)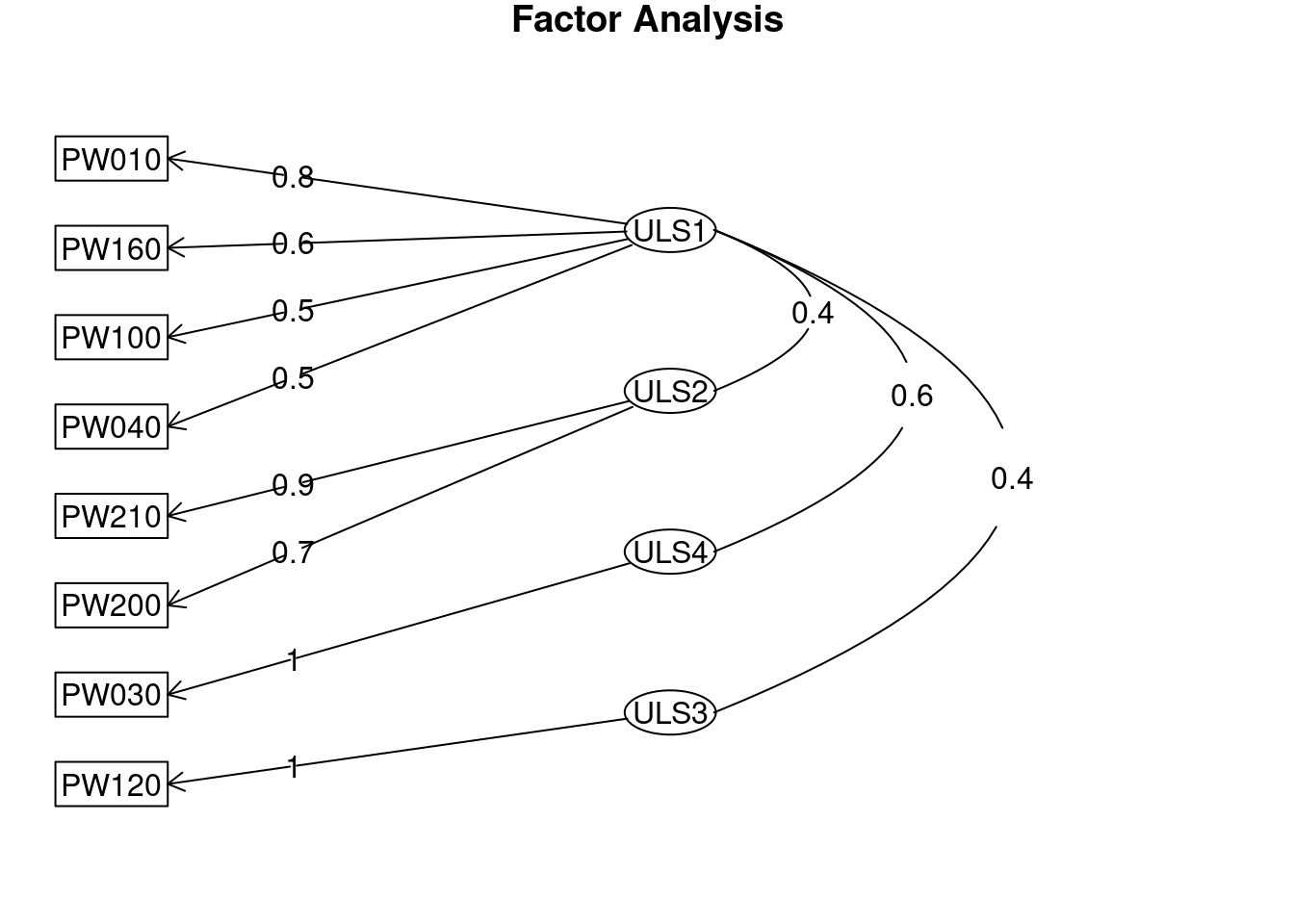
# Rotación ortogonal varimax:
AFE_varimax <- fa(matriz_correlaciones, nfactors = 4, n.obs = nrow(datos_AFE), rotate = "varimax", fm = "uls", alpha = 0.05)
AFE_varimaxFactor Analysis using method = uls
Call: fa(r = matriz_correlaciones, nfactors = 4, n.obs = nrow(datos_AFE),
rotate = "varimax", fm = "uls", alpha = 0.05)
Standardized loadings (pattern matrix) based upon correlation matrix
ULS1 ULS2 ULS4 ULS3 h2 u2 com
PW010 0.74 0.10 0.27 0.09 0.65 0.3543 1.3
PW030 0.39 0.13 0.90 0.11 1.00 0.0045 1.4
PW040 0.54 0.31 0.22 0.06 0.44 0.5587 2.0
PW100 0.54 0.13 0.19 0.17 0.38 0.6242 1.6
PW120 0.25 0.13 0.10 0.95 1.00 0.0045 1.2
PW160 0.58 0.18 0.04 0.14 0.39 0.6099 1.3
PW200 0.15 0.71 0.09 0.11 0.55 0.4544 1.2
PW210 0.25 0.89 0.06 0.05 0.87 0.1317 1.2
ULS1 ULS2 ULS4 ULS3
SS loadings 1.77 1.49 1.00 1.00
Proportion Var 0.22 0.19 0.12 0.12
Cumulative Var 0.22 0.41 0.53 0.66
Proportion Explained 0.34 0.28 0.19 0.19
Cumulative Proportion 0.34 0.62 0.81 1.00
Mean item complexity = 1.4
Test of the hypothesis that 4 factors are sufficient.
df null model = 28 with the objective function = 2.48 with Chi Square = 33268.91
df of the model are 2 and the objective function was 0.01
The root mean square of the residuals (RMSR) is 0.01
The df corrected root mean square of the residuals is 0.03
The harmonic n.obs is 13443 with the empirical chi square 53.96 with prob < 1.9e-12
The total n.obs was 13443 with Likelihood Chi Square = 111.81 with prob < 5.3e-25
Tucker Lewis Index of factoring reliability = 0.954
RMSEA index = 0.064 and the 95 % confidence intervals are 0.052 0.076
BIC = 92.8
Fit based upon off diagonal values = 1
Measures of factor score adequacy
ULS1 ULS2 ULS4 ULS3
Correlation of (regression) scores with factors 0.83 0.92 0.97 0.99
Multiple R square of scores with factors 0.69 0.86 0.95 0.98
Minimum correlation of possible factor scores 0.37 0.71 0.90 0.97fa.diagram(AFE_varimax)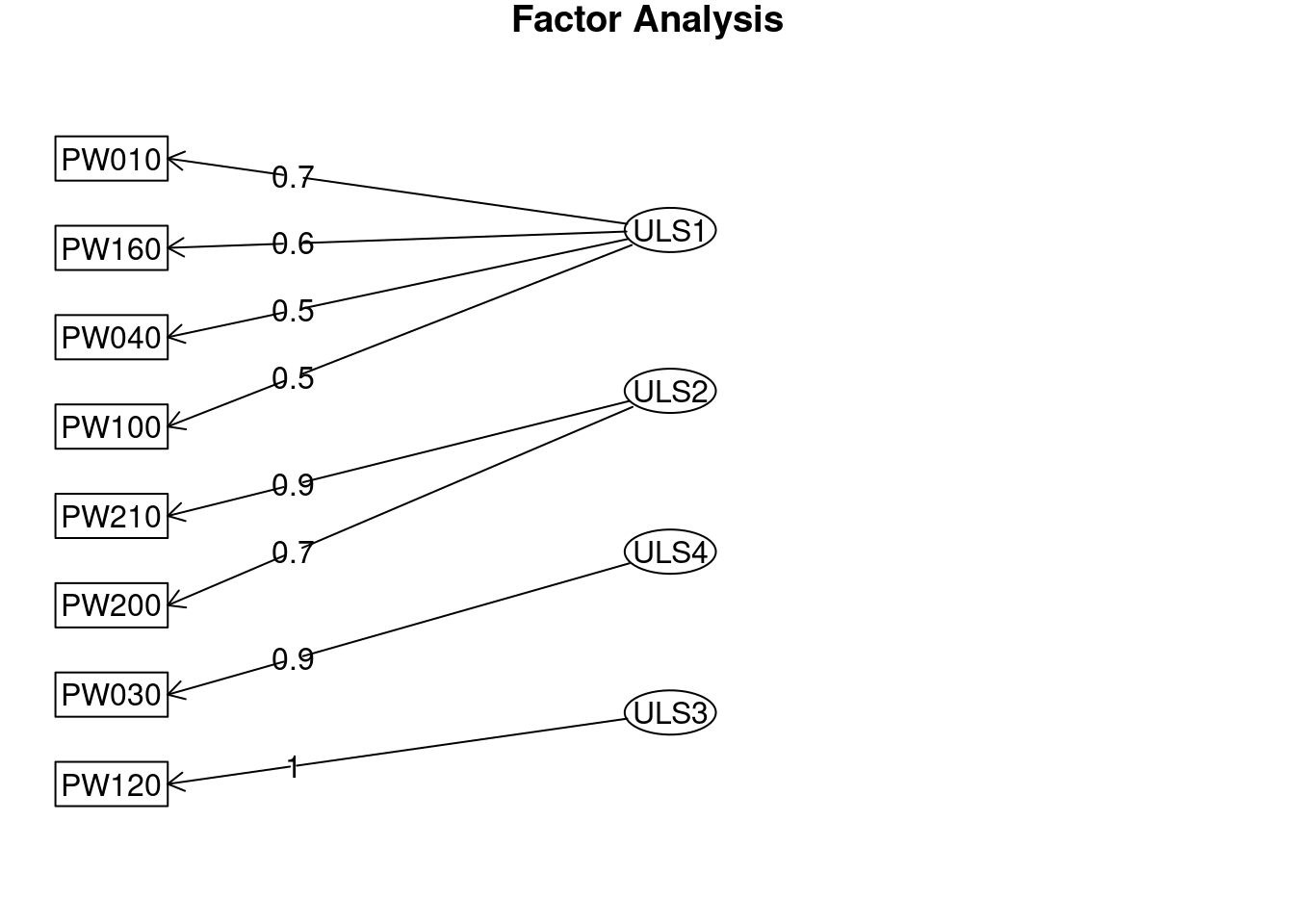
Resultados AFE:
El resultado usando tanto la rotación oblicua como la ortogonal es similar (en la ortogonal vemos como los factores ya no están correlacionados - porque no se les permite estarlo). En ambos casos, el ajuste, siguiendo los índices de bondad del mismo, es muy bueno: RMSEA y RMSR inferiores a 0,08 y TLI mayor a 0,95.
Análisis Factorial Confirmatorio (CFA):
La diferencia fundamental entre el EFA y el CFA, es que el EFA, como su propio nombre indica, es una técnica exploratoria: con ella queremos conocer la estructura de factores o variables latentes subyacente a los datos. Sin embargo, con el CFA, nosotros testamos si una determinada estructura factorial ajusta bien o no a los datos. Esto es, en este segundo caso, nosotros debemos imponer una estructura fatorial de antemano. Recurriendo a los índices de bondad del ajusto comprobaremos si dicha estructura es o no correcta.
Paso 1: determinar un método de extracción de factores:
Al igual que hacíamos con el EFA, con el CFA también debemos determinar un método concreto para extraer los factores. Con el fin de establecer un método u otro, llevaremos a cabo un test de Mardia: si existiera normalidad multivariante, podríamos utilizar Máxima Verosimilitud. Si nuestros datos no fuesen normales, Mínimo Cuadrados No Ponderados sería una buena opción.
mardia(datos_AFC, na.rm = TRUE)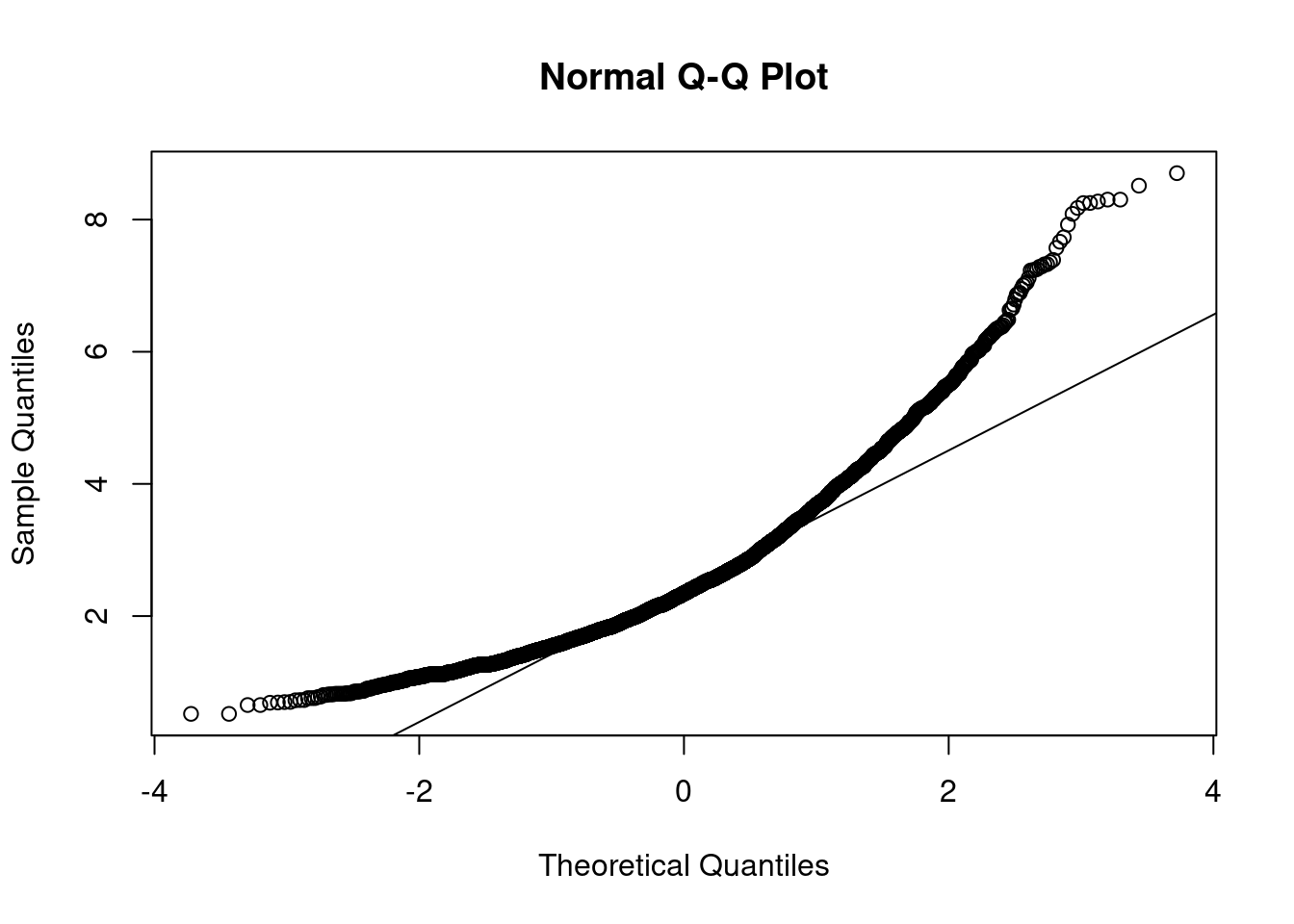
Call: mardia(x = datos_AFC, na.rm = TRUE)
Mardia tests of multivariate skew and kurtosis
Use describe(x) the to get univariate tests
n.obs = 5107 num.vars = 8
b1p = 11.59 skew = 9861.08 with probability <= 0
small sample skew = 9868.16 with probability <= 0
b2p = 126.63 kurtosis = 131.71 with probability <= 0ks.test(datos_AFC, pnorm)
Asymptotic one-sample Kolmogorov-Smirnov test
data: datos_AFC
D = 0.95624, p-value < 2.2e-16
alternative hypothesis: two-sidedComo podíamos esperar los resultados son idénticos a los obtenidos con la mitad de la muestra destinada al EFA: rechazamos la hipótesis nula de normalidad multivariante (al ser los p-valores inferiores a los niveles de significación habituales). Por ello, tampoco podemos usar Máxima Verosimilitud para el CFA, y usaremos, de nuevo, Mínimos Cuadrados No Ponderados (ULS).
Paso 2: Probar una o varias estructuras factoriales:
Vamos a plantear 3 modelos diferentes: uno que replique la estructura factorial planteada en el EFA, otro de un solo factor y otro de dos factores.
Para comparar modelos nos vamos a fijar en los índices de bondad del ajuste. Al igual que comentamos con el EFA: la situación óptima es aquella en la que los índices SRMR y RMSEA son inferiores a 0,08 - cuanto más bajos mejor -, y los índices TLI y CFI son superiores a 0,95 - cuanto más altos mejor.
Modelo con los cuatro factores que muestra el Exploratorio:
# Especificamos el modelo:
modelo_4F_AFE <- "Factor1 =~ PW010 + PW040 + PW100 + PW160
Factor2 =~ PW200 + PW210
Factor3 =~ PW120
Factor4 =~ PW030"
# Realizamos el factorial:
factorial_4F_AFE <- cfa(modelo_4F_AFE, datos_AFC, estimator = "ULS", orthogonal = FALSE)
summary(factorial_4F_AFE, fit.measures = TRUE, standardized = TRUE)lavaan 0.6.17 ended normally after 31 iterations
Estimator ULS
Optimization method NLMINB
Number of model parameters 20
Used Total
Number of observations 5107 13440
Model Test User Model:
Test statistic 2798.941
Degrees of freedom 16
P-value (Unknown) NA
Model Test Baseline Model:
Test statistic 244573.959
Degrees of freedom 28
P-value NA
User Model versus Baseline Model:
Comparative Fit Index (CFI) 0.989
Tucker-Lewis Index (TLI) 0.980
Root Mean Square Error of Approximation:
RMSEA 0.185
90 Percent confidence interval - lower 0.179
90 Percent confidence interval - upper 0.190
P-value H_0: RMSEA <= 0.050 0.000
P-value H_0: RMSEA >= 0.080 1.000
Standardized Root Mean Square Residual:
SRMR 0.036
Parameter Estimates:
Standard errors Standard
Information Expected
Information saturated (h1) model Unstructured
Latent Variables:
Estimate Std.Err z-value P(>|z|) Std.lv Std.all
Factor1 =~
PW010 1.000 1.230 0.729
PW040 0.902 0.006 154.059 0.000 1.109 0.651
PW100 0.990 0.006 158.608 0.000 1.217 0.619
PW160 0.709 0.005 139.082 0.000 0.872 0.552
Factor2 =~
PW200 1.000 1.705 0.741
PW210 0.988 0.008 127.508 0.000 1.685 0.912
Factor3 =~
PW120 1.000 2.341 1.000
Factor4 =~
PW030 1.000 1.936 1.000
Covariances:
Estimate Std.Err z-value P(>|z|) Std.lv Std.all
Factor1 ~~
Factor2 1.082 0.008 135.914 0.000 0.516 0.516
Factor3 1.427 0.009 153.160 0.000 0.496 0.496
Factor4 1.610 0.010 165.798 0.000 0.676 0.676
Factor2 ~~
Factor3 1.210 0.011 109.986 0.000 0.303 0.303
Factor4 1.058 0.011 98.275 0.000 0.320 0.320
Factor3 ~~
Factor4 1.399 0.014 99.975 0.000 0.309 0.309
Variances:
Estimate Std.Err z-value P(>|z|) Std.lv Std.all
.PW010 1.336 0.019 69.104 0.000 1.336 0.469
.PW040 1.676 0.018 92.327 0.000 1.676 0.577
.PW100 2.389 0.019 124.496 0.000 2.389 0.617
.PW160 1.738 0.016 105.875 0.000 1.738 0.695
.PW200 2.383 0.030 78.692 0.000 2.383 0.450
.PW210 0.577 0.030 19.415 0.000 0.577 0.169
.PW120 0.000 0.000 0.000
.PW030 0.000 0.000 0.000
Factor1 1.512 0.013 113.445 0.000 1.000 1.000
Factor2 2.908 0.027 108.321 0.000 1.000 1.000
Factor3 5.478 0.014 391.452 0.000 1.000 1.000
Factor4 3.748 0.014 267.783 0.000 1.000 1.000semPlot::semPaths(factorial_4F_AFE,
whatLabels = "est",
sizeMan = 3.25,
node.width = 1,
edge.label.cex = .75,
style = "ram",
mar = c(10, 5, 10, 5)
)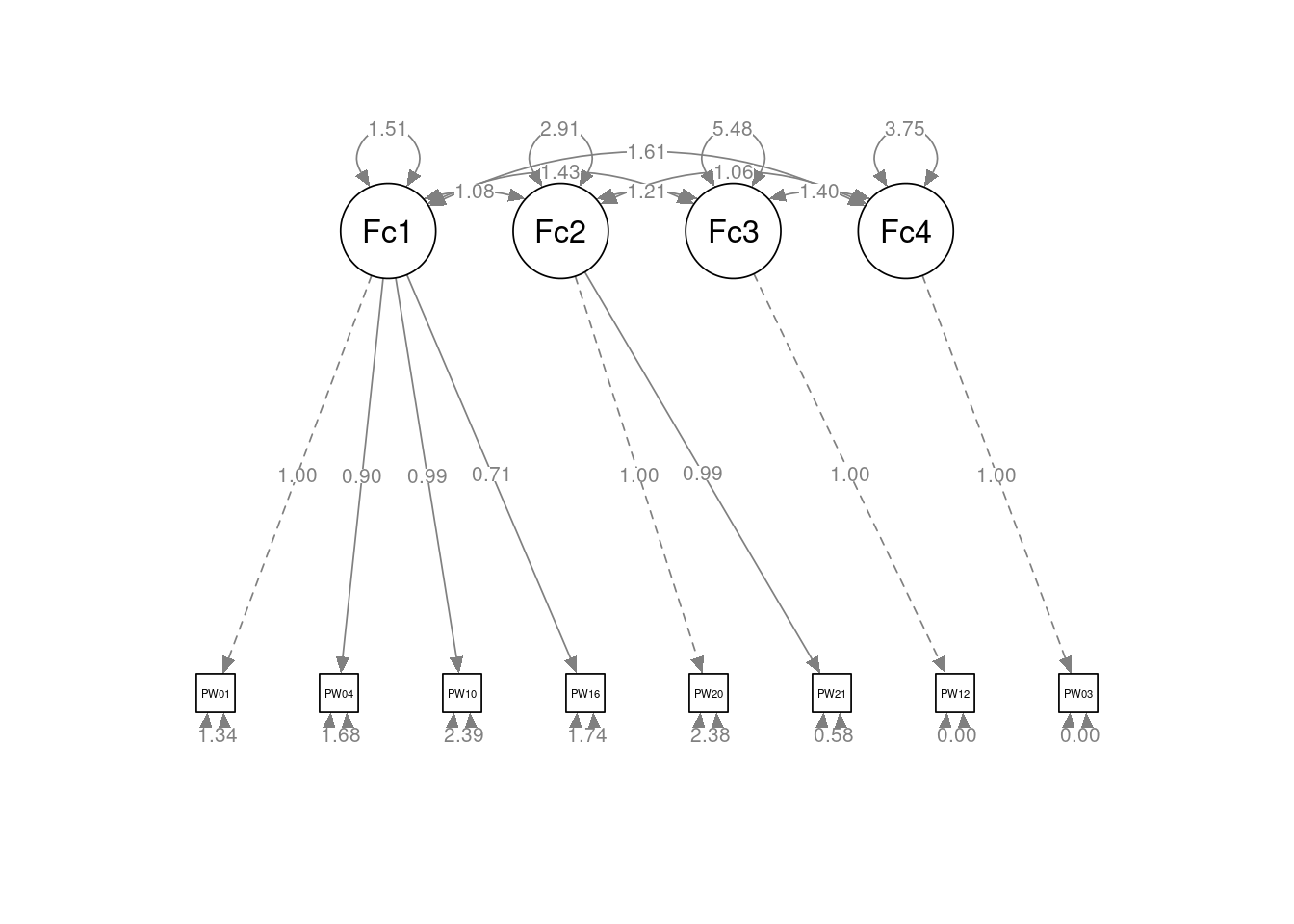
Se nos despliega una gran cantidad de información, pero, para facilitar el análisis, nos fijaremos simplemente en los índices de bondad del ajuste. Siguiendo dichos índices, el ajuste parece bueno: SRMR < 0,08, y TLI y CFI > 0,95. Sin embargo, RMSEA es mayor a 0,8
Modelo con un solo factor:
# Planteamos el modelo:
modelo_1F <- "Factor =~ PW010 + PW030 + PW040 + PW100 + PW120 + PW160 + PW200 + PW210"
# Realizamos el factorial:
factorial_1F_AFE <- cfa(modelo_1F, datos_AFC, estimator = "ULS", orthogonal = FALSE)
summary(factorial_1F_AFE, fit.measures = TRUE, standardized = TRUE)lavaan 0.6.17 ended normally after 35 iterations
Estimator ULS
Optimization method NLMINB
Number of model parameters 16
Used Total
Number of observations 5107 13440
Model Test User Model:
Test statistic 19921.783
Degrees of freedom 20
P-value (Unknown) NA
Model Test Baseline Model:
Test statistic 244573.959
Degrees of freedom 28
P-value NA
User Model versus Baseline Model:
Comparative Fit Index (CFI) 0.919
Tucker-Lewis Index (TLI) 0.886
Root Mean Square Error of Approximation:
RMSEA 0.441
90 Percent confidence interval - lower 0.436
90 Percent confidence interval - upper 0.447
P-value H_0: RMSEA <= 0.050 0.000
P-value H_0: RMSEA >= 0.080 1.000
Standardized Root Mean Square Residual:
SRMR 0.084
Parameter Estimates:
Standard errors Standard
Information Expected
Information saturated (h1) model Unstructured
Latent Variables:
Estimate Std.Err z-value P(>|z|) Std.lv Std.all
Factor =~
PW010 1.000 1.153 0.683
PW030 1.036 0.006 160.123 0.000 1.195 0.617
PW040 0.933 0.006 154.647 0.000 1.075 0.631
PW100 1.002 0.006 158.516 0.000 1.156 0.588
PW120 0.995 0.006 158.139 0.000 1.147 0.490
PW160 0.737 0.005 139.432 0.000 0.849 0.537
PW200 1.021 0.006 159.425 0.000 1.177 0.512
PW210 1.017 0.006 159.238 0.000 1.173 0.635
Variances:
Estimate Std.Err z-value P(>|z|) Std.lv Std.all
.PW010 1.518 0.018 84.056 0.000 1.518 0.533
.PW030 2.321 0.018 126.206 0.000 2.321 0.619
.PW040 1.749 0.017 100.078 0.000 1.749 0.602
.PW100 2.535 0.018 140.204 0.000 2.535 0.655
.PW120 4.162 0.018 231.056 0.000 4.162 0.760
.PW160 1.777 0.016 110.391 0.000 1.777 0.711
.PW200 3.905 0.018 213.996 0.000 3.905 0.738
.PW210 2.040 0.018 112.034 0.000 2.040 0.597
Factor 1.330 0.011 116.555 0.000 1.000 1.000semPlot::semPaths(factorial_1F_AFE,
whatLabels = "est",
sizeMan = 3.25,
node.width = 1,
edge.label.cex = .75,
style = "ram",
mar = c(10, 5, 10, 5)
)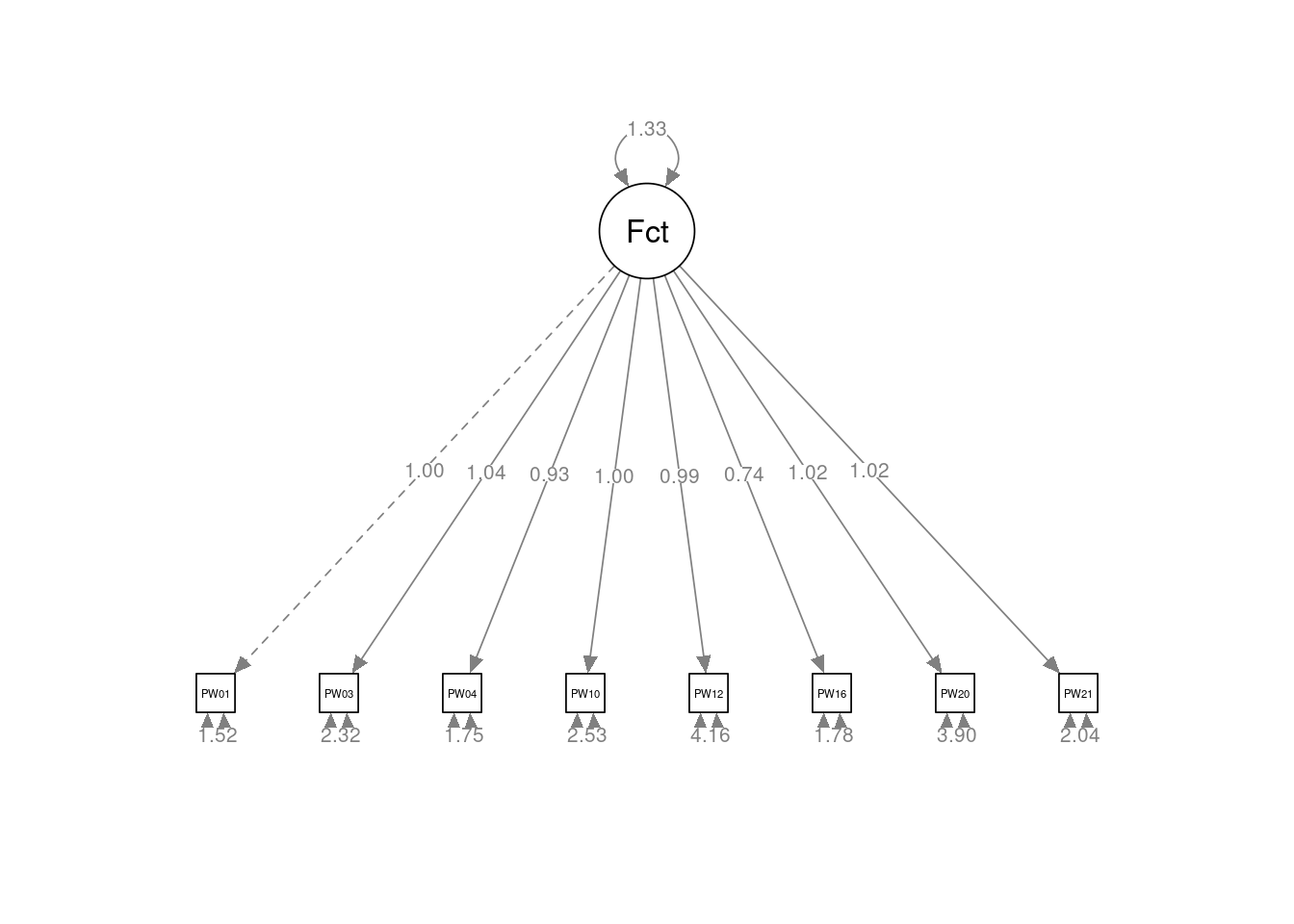
Los índices de bondad del ajuste presentan todos peores valores que el modelo de 4 factores obtenido en el AFE: RMSEA = 0,441; SRMR = 0,084; CFI = 0,919; TLI = 0,886
Modelo con dos factores:
Planteamos un modelo con dos factores: uno que englobe los tres items relacionados con la vivienda, y otro que englobe el resto de ítems.
# Planteamos el modelo:
modelo_2F <- "factor_vivienda =~ PW040 + PW200 + PW210
factor_miscelanea =~ PW010 + PW030 + PW100 + PW120 + PW160"
# Realizamos el factorial:
factorial_2F <- cfa(modelo_2F, datos_AFC, estimator = "ULS", orthogonal = FALSE)
summary(factorial_2F, fit.measures = TRUE, standardized = TRUE)lavaan 0.6.17 ended normally after 35 iterations
Estimator ULS
Optimization method NLMINB
Number of model parameters 17
Used Total
Number of observations 5107 13440
Model Test User Model:
Test statistic 12204.349
Degrees of freedom 19
P-value (Unknown) NA
Model Test Baseline Model:
Test statistic 244573.959
Degrees of freedom 28
P-value NA
User Model versus Baseline Model:
Comparative Fit Index (CFI) 0.950
Tucker-Lewis Index (TLI) 0.927
Root Mean Square Error of Approximation:
RMSEA 0.354
90 Percent confidence interval - lower 0.349
90 Percent confidence interval - upper 0.360
P-value H_0: RMSEA <= 0.050 0.000
P-value H_0: RMSEA >= 0.080 1.000
Standardized Root Mean Square Residual:
SRMR 0.073
Parameter Estimates:
Standard errors Standard
Information Expected
Information saturated (h1) model Unstructured
Latent Variables:
Estimate Std.Err z-value P(>|z|) Std.lv Std.all
factor_vivienda =~
PW040 1.000 1.121 0.658
PW200 1.300 0.009 146.358 0.000 1.458 0.634
PW210 1.306 0.009 146.386 0.000 1.465 0.792
factor_miscelanea =~
PW010 1.000 1.231 0.729
PW030 1.025 0.007 157.091 0.000 1.261 0.652
PW100 1.000 0.006 156.148 0.000 1.231 0.626
PW120 0.986 0.006 155.560 0.000 1.214 0.519
PW160 0.718 0.005 137.747 0.000 0.884 0.559
Covariances:
Estimate Std.Err z-value P(>|z|) Std.lv Std.all
factor_vivienda ~~
factor_misceln 0.920 0.006 142.840 0.000 0.667 0.667
Variances:
Estimate Std.Err z-value P(>|z|) Std.lv Std.all
.PW040 1.649 0.019 88.350 0.000 1.649 0.567
.PW200 3.166 0.023 138.155 0.000 3.166 0.598
.PW210 1.271 0.023 55.195 0.000 1.271 0.372
.PW010 1.333 0.019 69.586 0.000 1.333 0.468
.PW030 2.157 0.019 110.858 0.000 2.157 0.576
.PW100 2.355 0.019 122.927 0.000 2.355 0.608
.PW120 4.005 0.019 210.874 0.000 4.005 0.731
.PW160 1.717 0.016 104.214 0.000 1.717 0.687
factor_viviend 1.257 0.012 101.809 0.000 1.000 1.000
factor_misceln 1.515 0.013 115.828 0.000 1.000 1.000semPlot::semPaths(factorial_2F,
whatLabels = "est",
sizeMan = 3.25,
node.width = 1,
edge.label.cex = .75,
style = "ram",
mar = c(10, 5, 10, 5)
)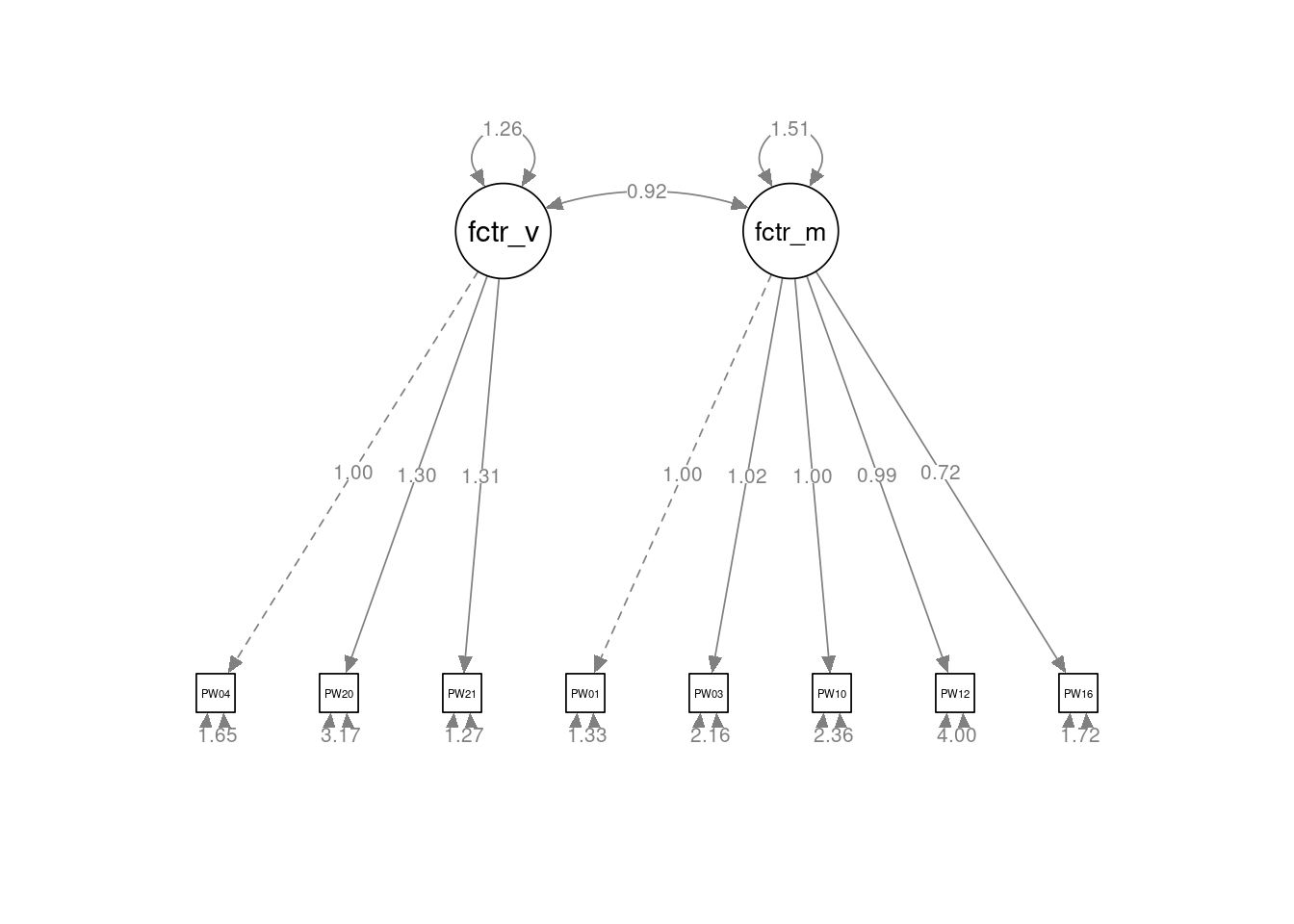
Los índices de bondad del ajuste presentan todos peores valores que el modelo de 4 factores obtenido en el AFE: RMSEA = 0,354; SRMR = 0,073; CFI = 0,950; TLI = 0,927
Resultados CFA:
Los índices de bondad del ajuste muestran que, de los tres modelos planteados, el modelo que refleja la estructura de los cuatro factores del AFE es el que mejor ajuste tiene.
Interpretamos los factores obtenidos tanto con el EFA como con el CFA:
Intentamos darle nombre a los factores, facilitando la interpretación de los resultados.
Los resultados entre el Análisis Factorial Exploratorio (EFA) y el Confirmatorio (CFA) concuerdan: el modelo que mejor ajusta es el que tiene cuatro factores:
Factor 1: variables PW010 (grado de satisfacción con la vida en la actualidad), PW040 (grado de satisfacción con la vivienda), PW100 (grado de satisfacción con el trabajo actual) y PW160 (grado de satisfacción con las relaciones personales). Factor “bienestar general/principal”.
Factor 2: variables PW200 (grado de satisfacción con las áreas recreativas o verdes de la zona en la que vive) y PW210 (grado de satisfacción con la calidad de la zona en la que vive). Factor “zona residencial”.
Factor 3: variable PW120 (grado de satisfacción con el tiempo que dispone para hacer lo que le gusta). Factor “tiempo libre”.
Factor 4: variable PW030 (grado de satisfacción con la situación económica en su hogar). Factor “situación económica”.
Conclusión
En este notebook se ha explicado como llevar a cabo una Reducción de la Dimensionalidad vía un Análisis Factorial, exponiendo las diferentes vías para hacerlo y las consideraciones a tener en cuenta. Se ha ilustrado con un caso práctico en el que se ha podido ir viendo la bondad del método empleado y que puede ser extrapolado a estudios futuros. El modelo inicial considerado tiene buenos indicadores de bondad de ajuste. Además interpretando los resultados parece razonable todos los coeficientes e indicadores obtenidos.
